2022年11月9日,我院草业科学系范吉标副教授在《Nucleic Acids Research》杂志发表了题为“Annotation and evaluation of base editing outcomes in multiple cell types using CRISPRbase”的数据库论文,该研究建立了一个大规模的单碱基编辑数据库CRISPRbase,其中收集了涵盖17个物种的186套高质量单碱基编辑数据,支持多种单碱基编辑系统比较的功能,用户可以比较多种单碱基编辑系统在特定基因位点的编辑效率和脱靶效应。该数据库中整合的数据资源将有助于生物学家研究单碱基编辑的编辑效率和脱靶效应,并为选择合适的单碱基编辑方案提供方向。
当前,CRISPR基因编辑技术因其较高的编辑效率而广泛应用于生命科学研究领域。但传统的CRISPR编辑技术因为需切割DNA双链而很难实现单碱基精准编辑,然而约有一半的遗传疾病是由单碱基突变(SNVs)导致的,大量动植物表型也是由于单碱基突变引起。然而,大多数SNVs深层机制尚不清楚,于是无需切割DNA就能实现碱基高效编辑的CRISPR单碱基编辑技术便应运而生。CRISPR单碱基编辑技术(CRISPR base editing,BE)是在CRISPR基因编辑技术基础上发展而来的能够实现单个碱基的替换编辑的基因编辑技术,包括实现C->T突变的胞嘧啶碱基编辑器(Cytosine Base Editors, CBE),A->G突变的腺嘌呤碱基编辑器(Adenine Base Editors, ABE)和C->G突变的胞嘧啶鸟嘌呤碱基编辑器(C-to-G base editors, CGBE)。随着CRISPR单碱基编辑技术的迅猛发展,该技术已广泛应用于人类、动物、植物和微生物的相关研究,CRISPR单碱基编辑的数据量也随之不断增大,从中准确找到自己所需要的信息,对相关研究者来说是个不小的挑战。
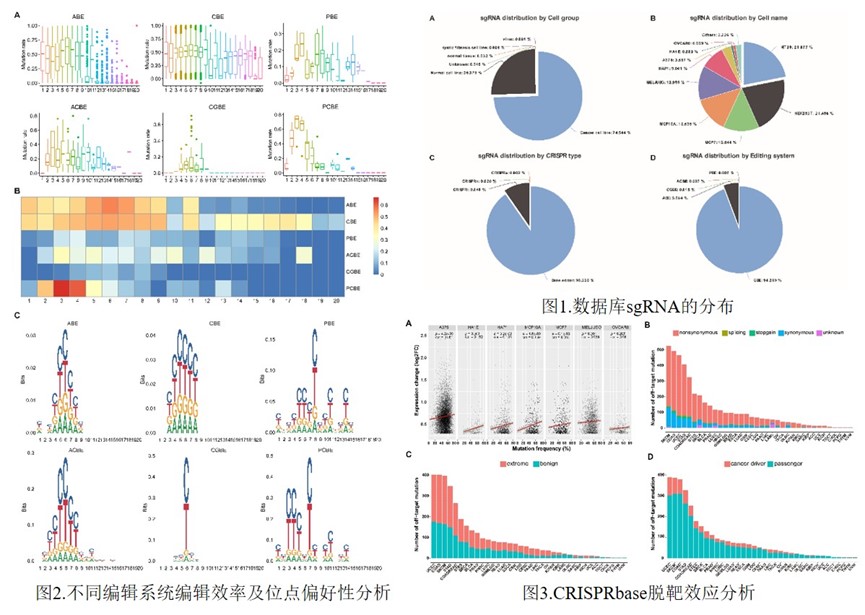
为解决这个问题,范吉标副教授联合北京大学第三医院、广东省农业科学院水稻研究所和中国医学科学院肿瘤医院等多家单位,通过收集、整理和分析相关数据,开发出了CRISPRbase单碱基编辑数据库(http://crisprbase.maolab.org)。该数据库目前记录了17个物种(包括人类、猪、羊、水稻等),50多个细胞/组织类型的1,252,935条单碱基编辑数据,收集自PubMed公开发表的186篇文献。该数据库集成了搜索、分析、提交、下载和统计等多种功能,研究团队基于sgRNA序列,分析了其在不同细胞类型、细胞系、组织、编辑系统和脱氨酶的分布(图1)、不同CRISPR单碱基编辑系统的在各编辑窗口(editing window)上各碱基位点的编辑效率和motif(图2)以及编辑效率和目的基因表达之间的关系,评估了脱靶效应导致的致病情况,并分析了这些致癌突变引起的极端和良性的比例(图3)。因此,CRISPRbase是一个CRISPR单碱基编辑的综合知识系统,将有助于基因编辑、基因功能分析、基因治疗、农作物育种等方面的研究工作。
范吉标副教授为该论文第一作者,北京大学第三医院毛凤彪研究员为通讯作者。
原文链接:https://doi.org/10.1093/nar/gkac967
数据库链接:http://crisprbase.maolab.org/
 苏公网安备 32100302010246号
苏公网安备 32100302010246号